6. Incluindo gráficos ao relatório
Agora que temos nosso ambiente configurado e já sabemos editar os chunks (trechos de códigos), poderemos utilizar a tabela com casos notificados de dengue para produzir gráficos e gerar outras tabelas.
Para incluir gráficos que serão gerados de forma automática pelo
R em seu documento, você deverá inserir o script
abaixo, após o subtítulo
### 1. Distribuição de casos por semana epidemiológica, com
os comandos que produzirão o gráfico. Tudo isso deverá estar dentro do
trecho de código (chunk) do seu documento, aquele delimitado
por três acentos graves. Veja o código que iremos utilizar para produzir
o gráfico e cole em seu arquivo .Rmd:
grafico_1 <- dengue |>
# Contando número de casos por ano e semana epidemiológica
count(ano_epi, sem_epi) |>
# Plotando visualização de gráfico por ano e semana epidemiológica
ggplot(aes(x = sem_epi, y = n, color = factor(ano_epi) )) +
# Adicionando linhas
geom_line() +
# Adicionando pontos
geom_point() +
# Aplicando novo tema para o gráfico
theme_minimal() +
# Adicionando rótulo para o eixo x
xlab("\nSemana epidemiológica") +
# Adicionando rótulo para o eixo y
ylab("") +
# Definindo o título da legenda
scale_color_discrete("Ano") +
# Definindo o intervalo de valores dos rótulos do eixo x
scale_x_continuous(breaks = c(1, seq(5, 50, 5)))
grafico_1
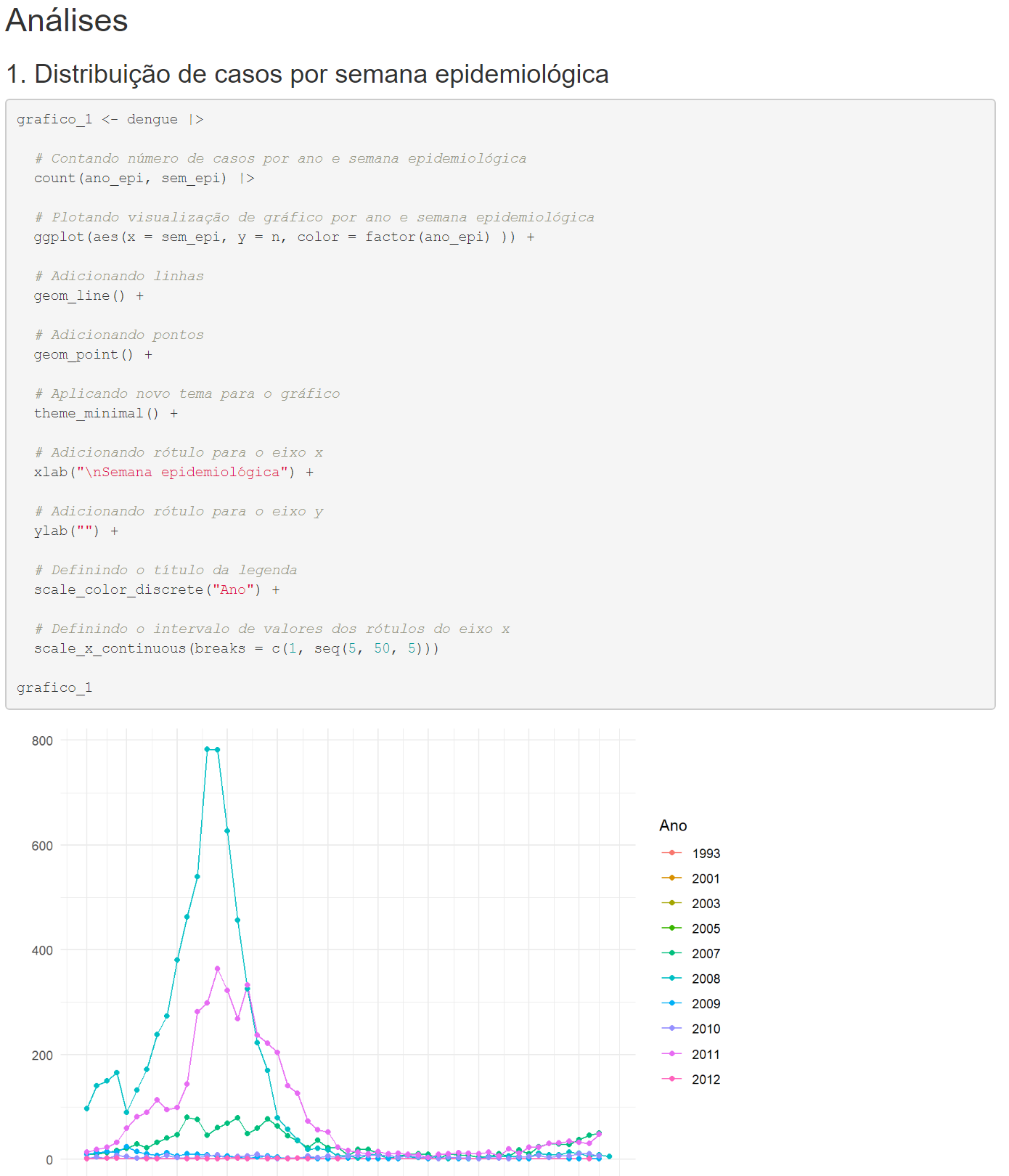
Pronto, agora verifique se seu arquivo .Rmd está
semelhante ao apresentado na Figura 54. Nela você poderá observar que
inserimos estes códigos após o subtítulo
### 1. Distribuição de casos por semana epidemiológica.
Veja a seguir:
Figura 54: Incluindo gráfico script após o subtítulo do relatório.

Agora renderize o seu documento: clique no botão knit e gere
um documento final do tipo .html que será semelhante ao
apresentado na Figura 55.
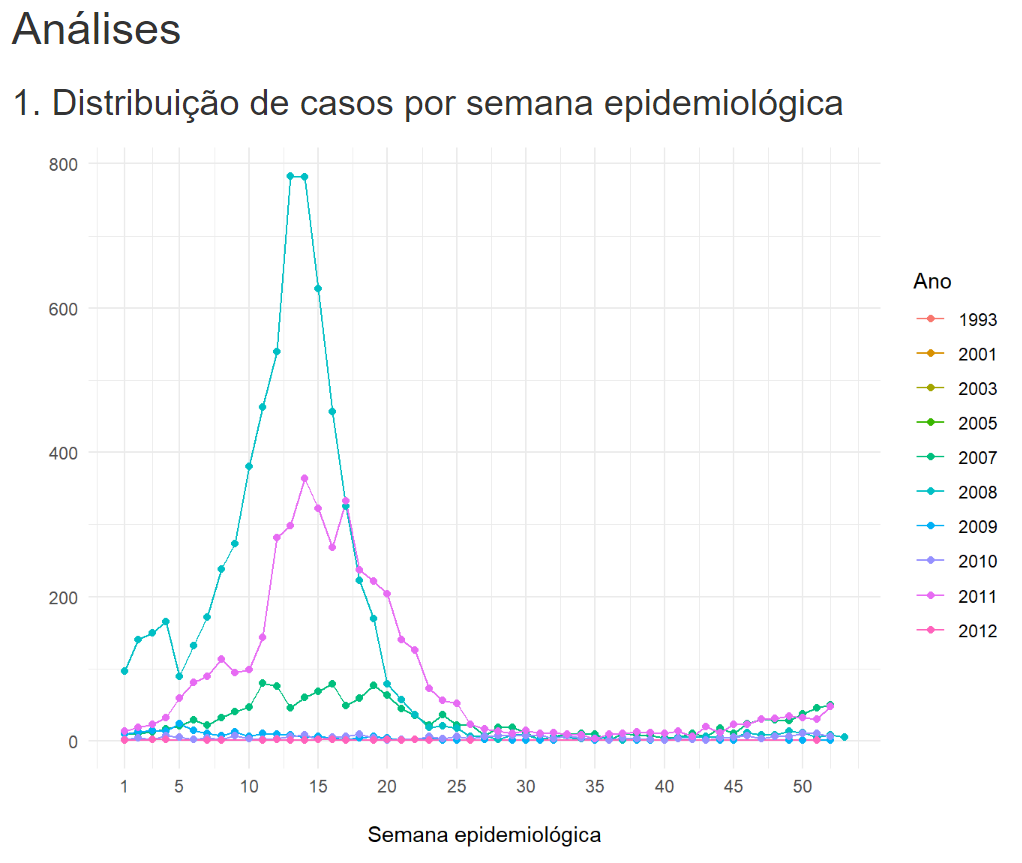
Figura 55: Renderização do script com inclusão de gráfico.
Observe na Figura 55 que o documento apresentará tanto o código
quanto o output deste código, ou seja, o gráfico. Conforme
vimos anteriormente, devemos incluir o argumento
echo = FALSE (Figura 56) no início do trecho de código para
que ele apresente somente o gráfico, dando uma estrutura de relatório a
ele. Observe a Figura 56 abaixo:
Figura 56: Renderização do script com a inclusão do argumento echo = FALSE na configuração do chunk.

Repita o processo e gere um novo arquivo do tipo .html
clicando no botão knit no menu superior do R.
Perceba que você obterá como resultado um documento semelhante ao
apresentado na Figura 57, ou seja, você verá que o código foi omitido e
que agora só conseguimos visualizar o gráfico que criamos.
Figura 57: Renderização do script com a inclusão do argumento echo = FALSE para produção gráfica.
Atenção
Caso tenha encontrado dificuldade de chegar a um arquivo com os scripts que utilizamos, não se preocupe e continue no curso!
Deixamos pronto para você um arquivo de estudo com todos os elementos
que aplicamos nesta subseção: o exemplo7.Rmd. Você poderá
encontrá-lo acessando o menu lateral “Arquivos” do Ambiente Virtual do
curso e fazer o download.
É possível ainda customizar o gráfico de saída com os seguintes argumentos:
fig.cap: título do gráficofig.height: altura do gráfico, em polegadasfig.widtht: largura do gráfico, em polegadasfig.align: alinhamento do gráfico. Você pode escolher as seguintes alternativas:right: alinhado à direita.left: alinhado à esquerdacenter: alinhado ao centro.
Para saber mais, acesse o curso “Visualização de dados de interesse para a Vigilância em Saúde”. Caso ainda não tenha feito o curso, sugerimos que se inscreva em https://www.abrasco.org.br/site/analise-de-dados-para-a-vigilancia-em-saude/.


